|
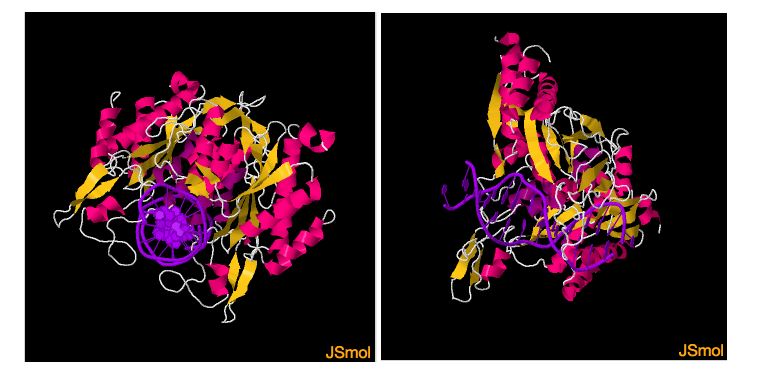
La reacción en cadena de la polimerasa, o PCR, amplifica un fragmento de ADN específico de una mezcla compleja. Primero, la mezcla se calienta para separar las cadenas de ADN. Se añaden dos cebadores oligonucleotídicos específicos diferentes que son complementarios a tramos de secuencia corta a cada lado del fragmento deseado. Después de bajar la temperatura, los cebadores se hibridan con el ADN donde se unen específicamente a los extremos de la secuencia objetivo deseada. Se añaden una ADN polimerasa termoestable y nucleótidos trifosfatos. La polimerasa extiende los cebadores y sintetiza nuevas cadenas de ADN complementarias. Al final de este primer ciclo, se producen dos moléculas de ADN de doble cadena que contienen la secuencia objetivo. Este ciclo de eventos se repite. La mezcla se calienta nuevamente para fundir el ADN bicatenario. Los cebadores se hibridan y la ADN polimerasa sintetiza nuevas cadenas complementarias. Al final del segundo ciclo, se producen cuatro moléculas de ADN de doble cadena que contienen la secuencia objetivo. En el tercer ciclo, la mezcla se calienta, los cebadores se hibridan y la ADN polimerasa sintetiza nuevas cadenas complementarias. Al final del tercer ciclo, se producen ocho moléculas de ADN de doble cadena que contienen la secuencia objetivo. Dos de estas moléculas son precisamente la longitud de la secuencia objetivo. En ciclos futuros esta población aumenta exponencialmente. Ciclo 4: calentamiento, hibridación, síntesis de ADN. Al final del quinto ciclo hay 22 fragmentos de ADN bicatenarios de la longitud correcta y 10 más largos. Ciclo 6, 10, 15, 20. . . Después de 30 ciclos, hay más de mil millones de fragmentos de la longitud correcta pero solo 60 más largos. Por lo tanto, el producto consiste en una secuencia objetivo esencialmente pura. La reacción en cadena de la polimerasa, o PCR, utiliza ciclos repetidos de calentamiento y enfriamiento para hacer muchas copias de una región específica de ADN. Primero, la temperatura se eleva a casi ebullición, lo que hace que el ADN bicatenario se separe o desnaturalice en cadenas individuales. Cuando se disminuye la temperatura, las secuencias cortas de ADN conocidas como cebadores se unen o recogen a coincidencias complementarias en la secuencia de ADN objetivo. Los cebadores colocan entre corchetes la secuencia de destino a copiar. A una temperatura ligeramente más alta, la enzima Taq polimerasa, que se muestra aquí en azul, se une a las secuencias preparadas y agrega nucleótidos para extender la segunda cadena. Esto completa el primer ciclo. En ciclos posteriores, el proceso de desnaturalización, recocido y extensión se repite para hacer copias adicionales de ADN. Después de 3 ciclos, la secuencia objetivo definida por los cebadores comienza a acumularse. Después de 30 ciclos, se producen hasta mil millones de copias de la secuencia objetivo a partir de una sola molécula de partida. Una técnica común en ingeniería genética es insertar un nuevo gen en un bucle de ADN bacteriano llamado plásmido. La herramienta molecular utilizada para cortar el ADN es una enzima de restricción como EcoRI. La enzima tiene una forma precisa que le permite correr a lo largo del surco de la doble hélice, escaneando en el caso de EcoRI la secuencia de letras base GAATTC. La enzima corta el plásmido en este punto específico, permitiendo que se inserte una nueva pieza de ADN. Cuando se corta, EcoRI deja un "final pegajoso". Esto ayuda al nuevo gen a unirse. Luego, las uniones se unen por otra enzima llamada ADN ligasa. La bacteria genéticamente modificada se cultiva en un medio de cultivo. Muy rápidamente se pueden producir grandes cantidades de bacterias, cada una con una copia del gen insertado. Las bacterias fabrican debidamente cualquier proteína que codifique el gen Enzima de restricción (1ERI)La imagen de la izquierda muestra una proteína relativamente pequeña con una mezcla de láminas beta y hélices alfa en su estructura. Mirando hacia abajo del eje de la hélice de ADN, la proteína tiene regiones flexibles que rodean el ADN y aparecen como "dedos" que "agarran" el ADN para realizar el proceso catalítico. Una vista del complejo con el eje de ADN de aproximadamente derecha a izquierda muestra que una cantidad significativa de contacto con el ADN involucra regiones flexibles. Sin embargo, en una sección, de aproximadamente la longitud de un sitio de restricción, una hélice alfa flanqueada por regiones flexibles se sienta en el surco principal del ADN, introduciendo una distorsión que potencialmente reduciría la energía libre para la reacción de escisión en cadena.
0 Comments
Leave a Reply. |
Categories
All
|
 RSS Feed
RSS Feed
