|
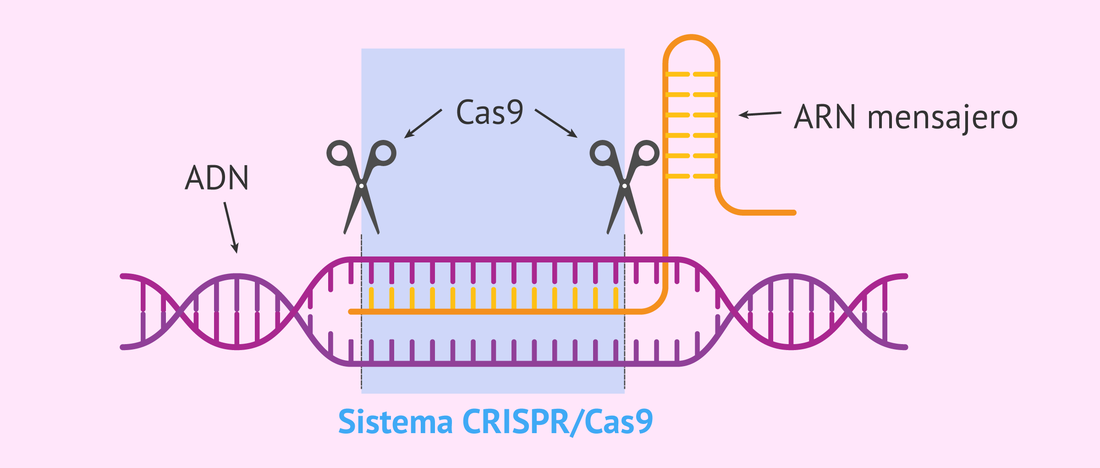
Resumen aportado por Spencer Seballos, asistente de enseñanza de la Universidad de Rice Se ha producido un debate significativo en la prensa y en revistas científicas sobre la prohibición de este método para la edición del genoma humano, y la demostración de los esfuerzos en embriones no viables sugiere que este método puede introducir errores sustanciales. No obstante, el método es ampliamente utilizado en la investigación de muchos tipos (véase la naturaleza reportaje por Cyranoski y Reardon 22 de de abril de 2015). ¿Qué tienen en común el ADN supuestamente basura, el sistema inmunitario bacteriano, la producción de queso y la edición del genoma? A primera vista, estos elementos parecen no estar relacionados, pero todos están asociados con secuencias de ADN denominadas "repeticiones palindrómicas cortas agrupadas regularmente espaciadas" (CRISPR) y una familia de proteínas conocida como proteínas asociadas a CRISPR (Cas) que se encuentran naturalmente en las bacterias. Un artículo de 2014 de Pennisi [ Science 341, 833 (2013)] describe la interesante historia detrás de la investigación que condujo a descubrir y dilucidar el sistema CRISPR / Cas9: los científicos de la compañía de ingredientes alimentarios Danisco descubrieron que podían inocular cepas bacterianas involucradas en la producción de alimentos contra infecciones bacteriófagas (virus) por exponiéndolos al ADN del fago, lo que demuestra que estas bacterias poseían alguna forma de sistema inmunitario adaptativo. Después de algo de experimentación, estos científicos descubrieron que "los procariotas parecen haber desarrollado un sistema de 'inmunidad' basado en ácido nucleico mediante el cual la especificidad es dictada por el contenido del separador CRISPR [previamente pensado como ADN basura], mientras que la resistencia es proporcionada por el enzimático Cas maquinaria "[Barrangou et al., Science 315 , 1709 (2007)]. Los científicos que exploraron cómo funcionaba exactamente este sistema pronto descubrieron que una familia de enzimas Cas proporcionaba resistencia al escindir el ADN extraño; Se descubrió que una de estas enzimas, Cas9, tenía un método de acción más simple que otras enzimas Cas y ha sido el foco principal de investigaciones posteriores. En un mecanismo sorprendentemente sencillo descrito en este video de YouTube, la proteína Cas9 utiliza ARN guía especiales llamados crRNA, derivados de los separadores CRISPR y el ADN palindrómico, para cortar el ADN extraño bicatenario que coincide con el crRNA. En 2012, los científicos descubrieron que al agregar un ARN sintetizado de una sola guía (sgRNA) a una mezcla que contiene la enzima Cas9, estos complejos sgRNA-Cas9 podrían localizar y cortar sus objetivos de ADN previstos con alta precisión. Como muestra el video, los científicos pueden utilizar los mecanismos de reparación del ADN de la célula para agregar su propia plantilla de ADN a la hebra cortada, utilizando efectivamente el sistema CRISPR / Cas9 para editar el genoma de la célula. Este sistema es muy versátil y puede usarse para diferentes secuencias de ADN, así como con ADN en una variedad de organismos. Otros sistemas de edición de ADN que utilizan enzimas llamadas TALEN o motivos de dedos de zinc que se unen al ADN requieren proteínas únicas para cada secuencia de ADN diferente. CRISPR / Cas9, sin embargo, solo requiere un sgRNA único con la enzima Cas9 para poder editar cualquier secuencia de ADN objetivo. Además, se ha demostrado que CRISPR / Cas9 es eficaz en una amplia variedad de células y organismos modelo, incluidas bacterias, plantas, moscas de la fruta, pez cebra, ratones y múltiples líneas celulares humanas. Si bien dicho sistema parece ser una panacea inmediata para una amplia variedad de enfermedades genéticas, desde la anemia de células falciformes hasta la enfermedad de Huntington, existen limitaciones y muchas características que aún deben aclararse sobre el sistema CRISPR / Cas9 antes de que pueda implementarse en Un contexto clínico. (¡También debemos recordar que esta tecnología emergente ha sido estudiada y desarrollada por menos de tres años!) Como se resume en una revisión de 2014 realizada por Ma y colegas [Ma et al., FEBS J. 281, 5186-5193 (2014)], los usuarios potenciales de los métodos CRISPR / Cas9 deben tener en cuenta varias cosas que pueden afectar la especificidad y la eficiencia del sistema: Primero, sgRNA y Cas9 deben entregarse al mismo tiempo a los núcleos de células objetivo específicas, Un requisito que puede ser un desafío. Segundo, el ADN objetivo debe contener secuencias de ADN específicas; por lo tanto, la selección del sitio objetivo y el diseño de sgRNA son importantes para una alta eficiencia y especificidad. Finalmente, Cas9 puede interrumpir otras secuencias, y estos efectos en el ADN no objetivo deben ser considerados. Los desarrollos recientes de CRISPR / Cas9 incluyen el empleo de otras nucleasas Cas en lugar de Cas9 en este sistema [Lemak et al., Nucl. Acidos Res. 42 , 11144 (2014)], dirigidas a secuencias de ARN para la escisión en lugar de ADN [O'Connell et al., Nature 516, 263 (2014)], y utilizando el reconocimiento CRISPR con otras endonucleasas como FokI para aumentar la especificidad (Tsai et al. ., Nat. Biotechnol. 32 , 569 (2014)]. El rápido desarrollo de los sistemas CRISPR / Cas9 como herramienta para derribar, insertar y editar genes ha dado lugar a posibilidades revolucionarias en la edición del genoma, y la capacidad de editar secuencias de ADN fácilmente y al costo relativamente bajo de los métodos CRISPR / Cas9 no tiene precedentes. Quedan preguntas sobre hasta qué punto este método puede llegar científicamente: ¿Puede ser finalmente lo suficientemente seguro y específico para su uso en terapia génica clínica? Tal vez aún más significativas son las posibles cuestiones éticas que están empezando a surgir como el desarrollo de CRISPR / Cas9 continúa acelerándose: ¿En qué situaciones podría / s hould se puede utilizar en la terapia génica? Otras referencias de interés: Doudna & Charpentier, La nueva frontera de la edición del genoma con CRISPR-Cas9, Science 346 , 1077 (2014). Maddalo et al., Ingeniería in vivo de reordenamientos cromosómicos oncogénicos con el sistema CRISPR / Cas9, Nature 516 , 423 (2014) Sanchez-Rivera et al., Modelado rápido de eventos genéticos cooperantes en cáncer a través de la edición del genoma somático, Nature 516 , 428 (2014) Referencias para las estructuras cristalográficas de rayos X para CRISPR / Cas9 y sus complejos: Jinek et al., Las estructuras de las endonucleasas Cas9 revelan la activación conformacional mediada por ARN, Science 343 , 1215 (2014). Jackson et al., Estructura cristalina del complejo de vigilancia guiada por ARN CRISPR de Escherichia coli , Science 345 , 1473 (2014). Mulepati et al., Estructura cristalina de un complejo de vigilancia guiado por ARN CRISPR unido a un objetivo de ADNss, Science 345, 1479 (2014).
0 Comments
Leave a Reply. |
Categories
All
|
 RSS Feed
RSS Feed
